UCSC复现文章circRNA--引物/敲低/功能及修饰预测

本期GBhouse将对已发表文献circRNA详细信息进行复现,现在提几个问题:1.如何根据circRNA高通量测序在UCSC查找circRNA序列?2.circRNA成环如何验证?3.circRNA敲低引物如何设计?4.UCSC怎么预测circRNA功能位点(如IRES,miRNA结合)?
(复现文献信息)
1 收集文章中的circRNA信息
1.1 研究基因及对应基因组位置
通过全文,可知作者通过circRNA高通量测序筛选到可能在肝癌细胞中存在重要调控的circRNA(SCD-circRNA2)。复现文中主要研究的SCD-circRNA2,染色体位置信息:chr10:102122370-102122756。
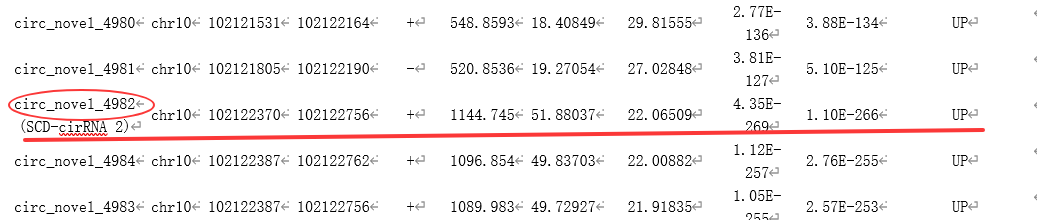
(图1.1 本文重点研究的circRNA基因信息)
1.2 SCD-circRNA2成环信息
为了生成适合SCD-circRNA2过表达的载体,扩增了SCD-circRNA 2的基因组区域,其反向剪接位点位于50 bp、200 bp或500 bp序列两侧。
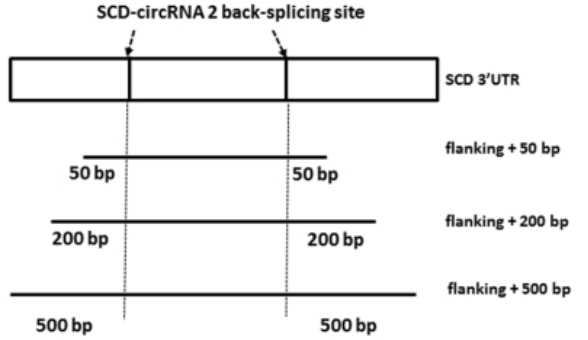
(图1.2 扩增SCD-circRNA2策略示意图)
此外,文中交代了SCD-circRNA2成环信息,即来源于母基因SCD外显子6的部分序列。
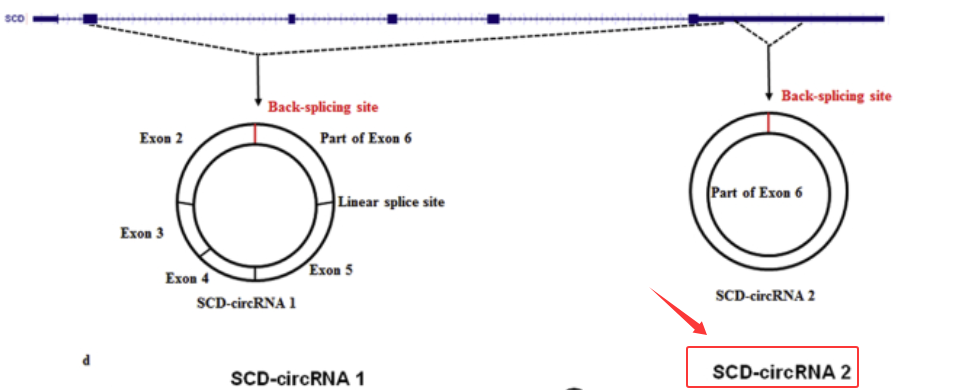
(图1.3 SCD-circRNA2来源示意图)
通过以上信息,小结:1. 本文研究目标SCD-circRNA2;2. 染色体位置:chr10:102122370-102122756,3. 扩增策略是反向剪接两侧的50-200-500bp。
2 使用UCSC查询和获取SCD-circRNA2基因序列
使用UCSC网站(https://genome.ucsc.edu/)查询和获取SCD-circRNA2基因序列,进行具体操作如下:
2.1 UCSC数据选择
将使用Human GRCh37/hg19 SCD-circRNA2基因信息及获取,一般情况下,均使用Human GRCh37/hg19(常用),而对于一些未知的基因信息可能需要尝试Human GRCh38/hg38。
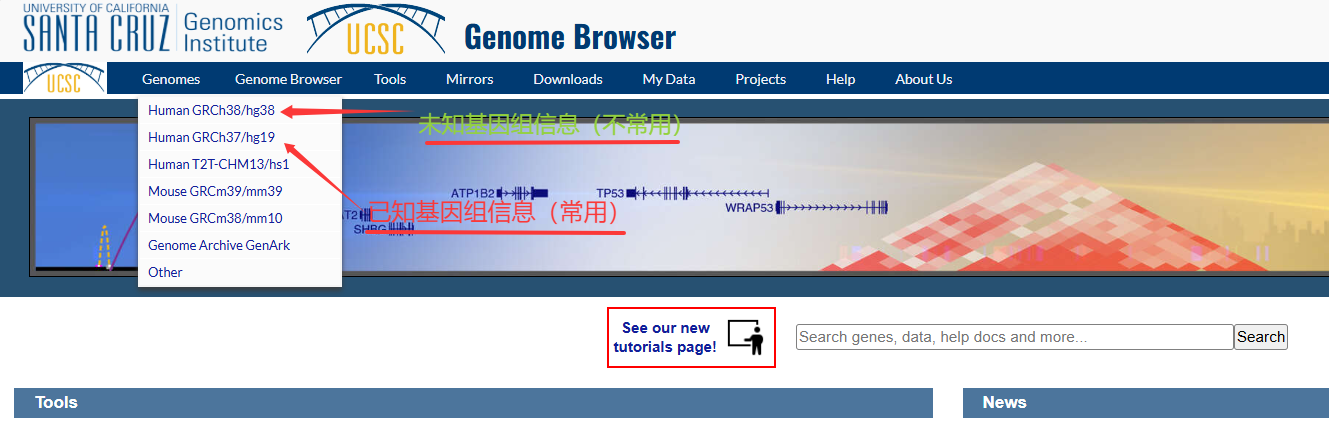
(图2.1 Human GRCh37/hg19查询序列信息)
2.2 查找确定SCD-circRNA2基因信息
根据文中信息,知道SCD-circRNA2在染色体位置:chr10:102122370-102122756,可见该位置信息粘贴到USCS查询对话框中进行查询,操作如下:
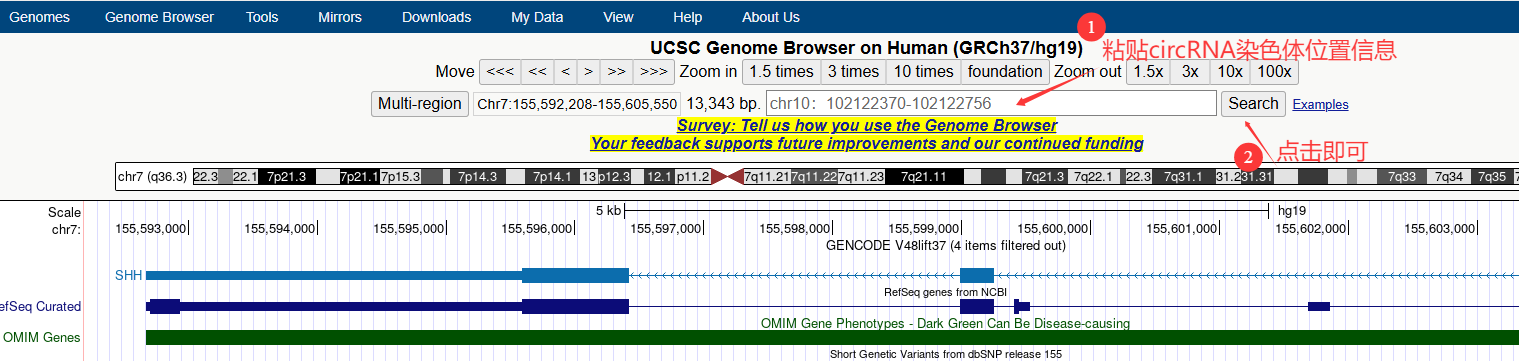
(图2.2 查询SCD-circRNA2基因序列操作示意图)
右击SCD即可见“get DNA for SCD”,点击该条目即可,如图2.3所示:
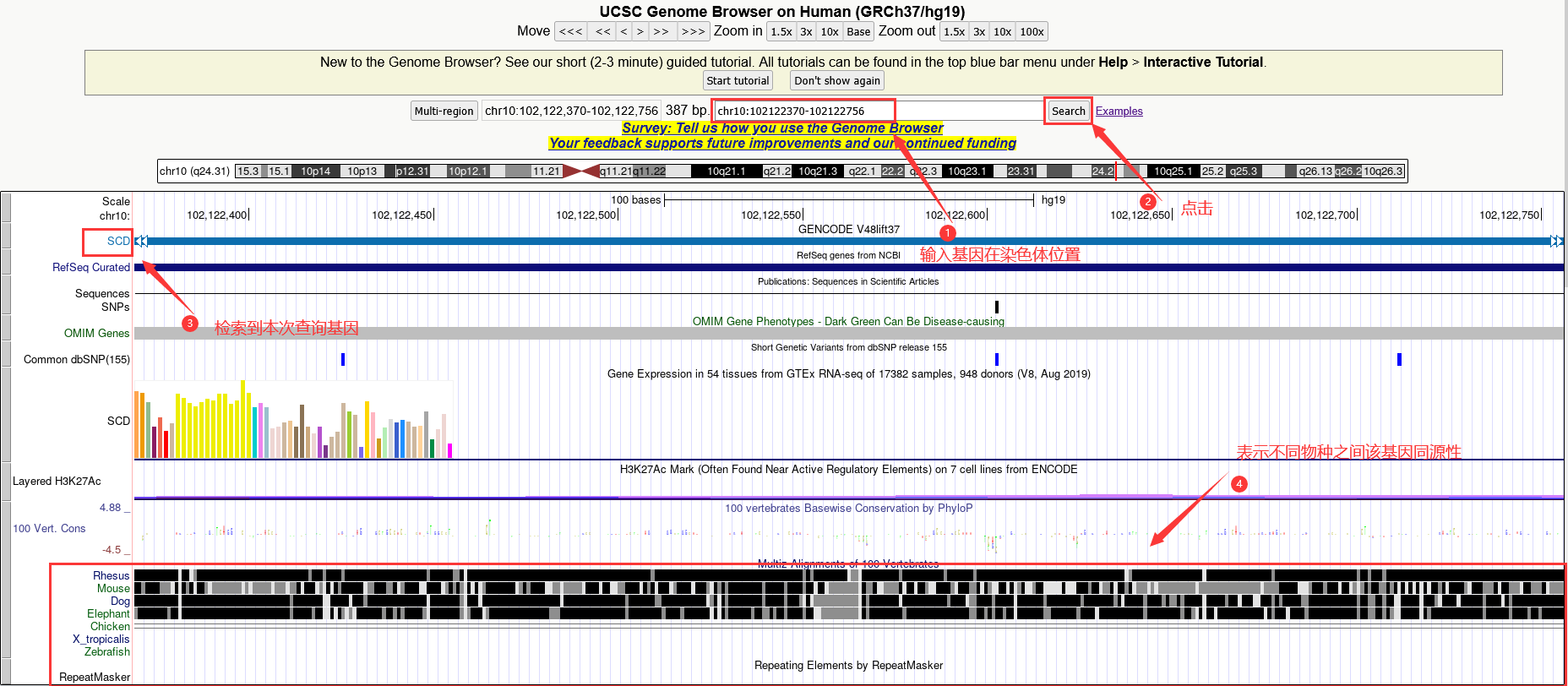
(图2.3 如何获取SCD基因序列示意图)
在接下来的操作界面,根据图2.4标记操作。首先是将SCD基因在染色体的位置更换为SCD-circRNA2所在位置(即前文交代的位置:chr10:102122370-102122756);其次是选择“all upper case”一般是正向(+)的意思,当然也有少部分是方向/负向(—);最后是点击“get DNA”即可获得SCD-circRNA2(chr10:102122370-102122756)碱基序列。

(图2.4 获取SCD-circRNA2 chr10:102122370-102122756碱基序列操作示意图)
>hg19_dna range=chr10:102122370-102122756(获取SCD-circRNA2碱基序列,可编辑)
TCCCTCCTGCACACAGAATGCTCAGGGTCACTGAACCACTGCTTCTCTTTTGAAAGTAGAGCTAGCTGCCACTTTCACGTGGCCTCCGCAGTGTCTCCACCTACACCCCTGTGCTCCCCTGCCACACTGATGGCTCAAGACAAGGCTGGCAAACCCTCCCAGAAACATCTCTGGCCCAGAAAGCCTCTCTCTCCCTCCCTCTCTCATGAGGCACAGCCAAGCCAAGCGCTCATGTTGAGCCAGTGGGCCAGCCACAGAGCAAAAGAGGGTTTATTTTCAGTCCCCTCTCTCTGGGTCAGAACCAGAGGGCATGCTGAATGCCCCCTGCTTACTTGGTGAGGGTGCCCCGCCTGAGTCAGTGCTCTCAGCTGGCAGTGCAATGCTTG(默认5’→3’)
3 如何实现circRNA反向组装
3.1 circRNA反向组装
一般情况是将3’端(剪接受体)截取100-200bp置于5’端(间接配体)(具体根据circRNA长度),这样重新组装的circRNA用于引物(primer)设计,剪接位置即为剪接位点(成环)。
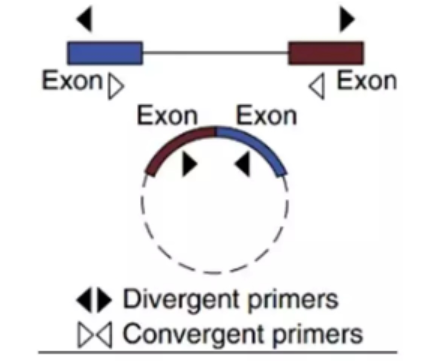
(图3.1 circRNA引物设计示意图)
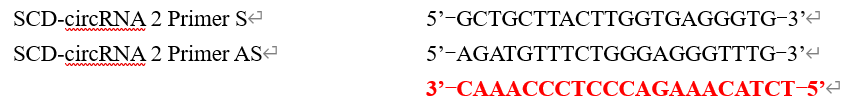
(图3.2 文中提供的SCD-circRNA2,红色为推文中将反向因为进行翻转)
SCD-circRNA2设计,将颠换3’端188bp粘贴至SCD-circRNA2的5’端(蓝色碱基)这样就形成了一个反向剪接(back-splice sequence)。

3.2 查找文中因为
根据文中提到的上游引物(GCTGCTTACTTGGTGAGGGTG)和下游引物(AGATGTTTCTGGGAGGGTTTG→CAAACCCTCCCAGAAACATCT(颠换方向)),查询引物对应的位置,引物设计的目的是为了验证是否能够成环。

4 获取的SCD-circRNA2序列准确性验证
使用UCSC“Tools-balt”;
(图4.1 UCSC序列比对/blast操作示意图)
将获取的SCD-circRNA2序列粘贴至比对对话框,注意UCSC识别fasta格式,需要在基因序列前边添加“>gene symbol”,然后点击Submit;
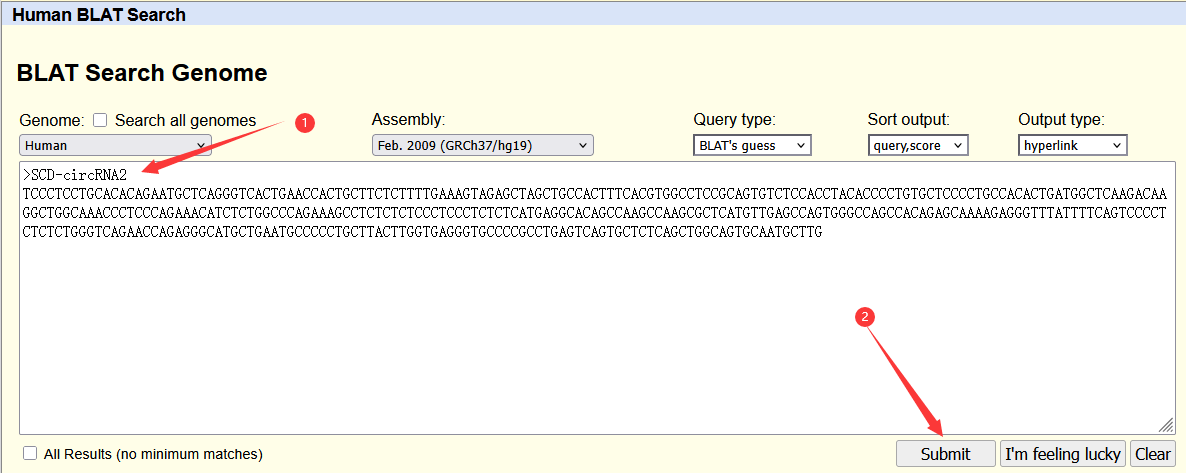
(图4.2 UCSC序列比对/blast操作设置示意图)
通过UCSC网站blast,发现获取的SCD-circRNA2序列与数据库能够达到百分百重合(图4.3);
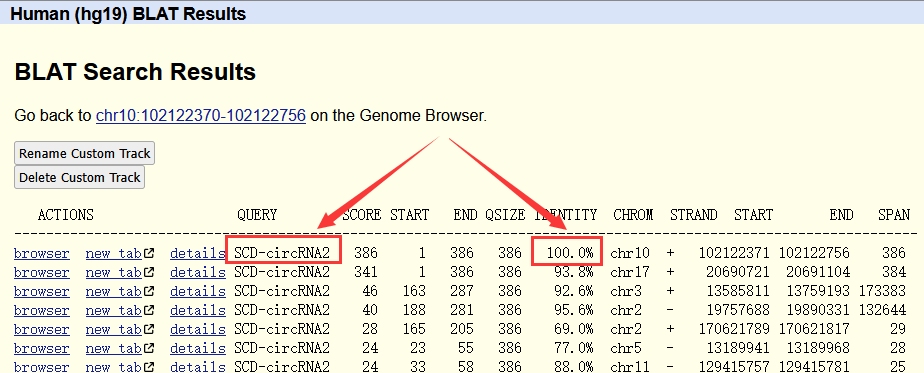
(图4.3 UCSC序列比对/blast结果示意图)
5 UCSC潜在功能及修饰预测
在UCSC完整还提供了预测circRNA的IRES,充当海绵吸附miRNA和m6A修饰(https://genome.ucsc.edu/s/atcgene/circbank_m6A_track)。只需要将circRNA所在基因组的位置信息(如SCD-circRNA2 chr10:102122370-102122756)粘贴进去即可查询。
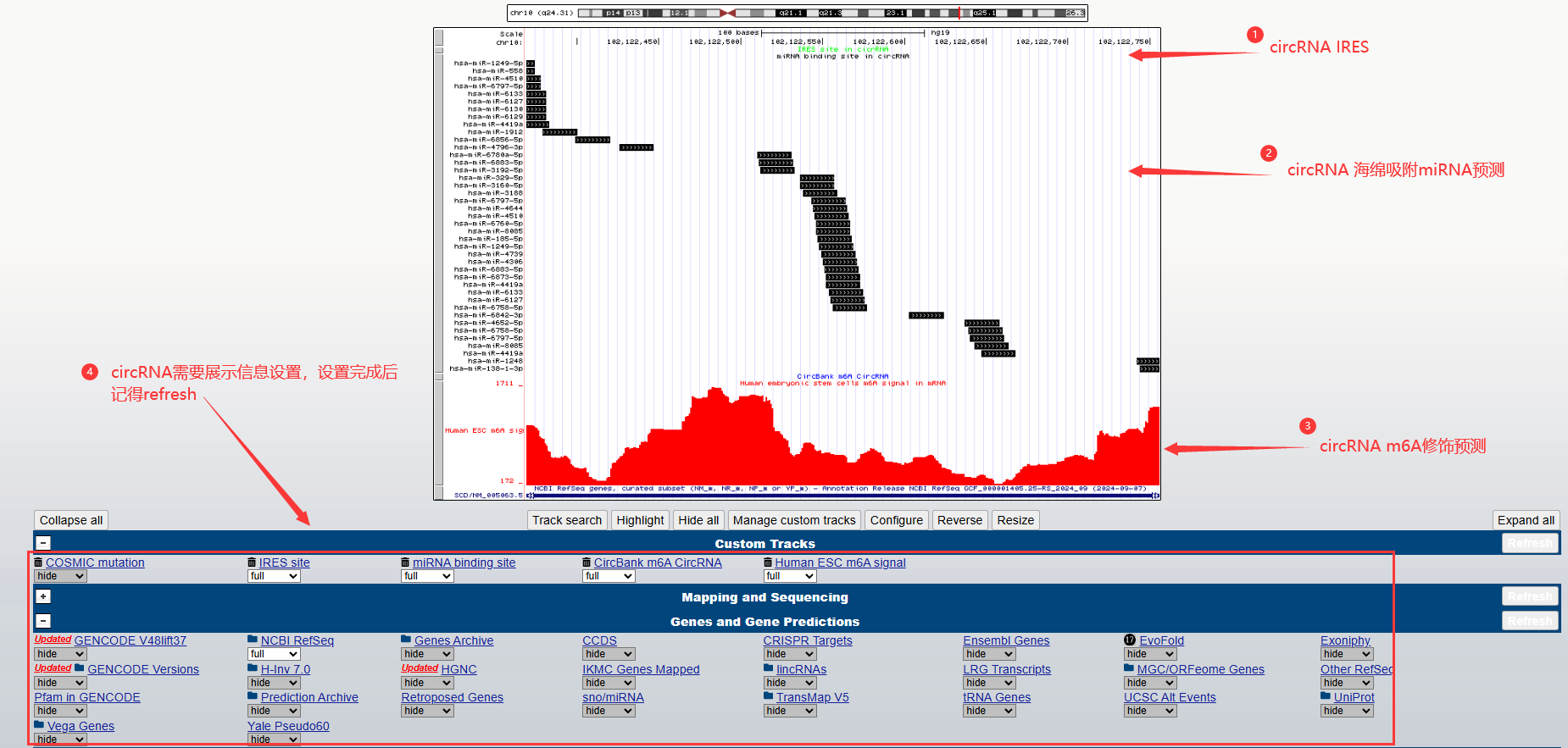
(图5.1 circRNA基本功能及修饰位点预测结果展示)
6 circRNA沉默/敲减位点的选择
首先根据文中提到的siRNA序列(短干扰RNA或沉默RNA,是一类双链RNA分子,长度为20-25个碱基对,类似于miRNA,并且在RNA干扰(RNAi)途径内操作)(siRNA1: (F)CAGUGCAAUGCUUGUCCCUTT/(R)AGGGACAAGCAUUGCACUGTT;siRNA2:(F) CAAUGCUUGUCCCUCCUGCTT/(R) GCAGGAGGGACAAGCAUUGTT)。可见circRNA的siRNA针对的是circRNA的剪接位点。

本期讲解结束,主要内容回顾:1. 根据circRNA基因组location查询序列;2. circRNA设计引物验证成环情况;3. circRNA如何利用UCSC预测miRNA结合,IRES和m6A。
每日一言
爱自己!!!做科研!!! 每文格言“和底层人打交道,要接受他们的占便宜,献媚,讨好,算计,同时欣赏他们的进取心、野心和不守规矩;和中产打交道,要接受他们的虚荣,攀比,虚伪,势力同时欣赏他们的情商,授权和左右逢源;和精英打交道,要接受他们的刻薄,傲慢,膨胀,藐视,同时欣赏他们的博学,智慧和永不言弃;和商人打交道,要接受他们的逐利,精明,善变,心黑,同时欣赏他们的冒险,果断和把握机会。不要和底层人讲逻辑,不要和中层人谈理想,不要和上层人谈感情。--冯唐《有底气》”如果有用,关注楼主GBhouse,点赞+讨论,攻击型人格请请请不要关注和阅读!!!

